在一种称为DNA折纸的技术中,研究人员一次又一次地折叠长链DNA,以构建各种微小的3D结构,包括微型生物传感器和药物输送容器。DNA折纸技术于2006年在加利福尼亚理工学院开创,在过去十年中吸引了数百名新研究人员,他们渴望建造可以检测和治疗人体疾病,评估污染物对环境的影响并协助开展研究的容器和传感器。许多其他生物学应用。
尽管DNA折纸的原理很简单,但该技术用于设计新结构的工具和方法并不总是容易掌握的,也没有得到充分的文献证明。此外,对这种方法不熟悉的科学家们没有单一的参考文献,他们只能寻求建立DNA结构的最有效方法以及如何避免可能浪费数月甚至数年研究的陷阱。
这就是为什么美国国家标准与技术研究院(NIST)的研究人员Jacob Majikes和Alex Liddle编写了有关DNA折纸已有多年经验的第一本详细教程的原因。他们的综合报告提供了使用最新工具设计DNA折纸纳米结构的分步指南。Majikes和Liddle在1月8日的“国家标准技术学院的研究”杂志上描述了他们的工作。
Majikes说:“我们希望将人们开发的所有工具都放在一个地方,并解释传统期刊文章中您不能说的事情。”“评论文件可能会告诉您每个人都做过的所有事情,但它们并没有告诉您人们是如何做到的。”
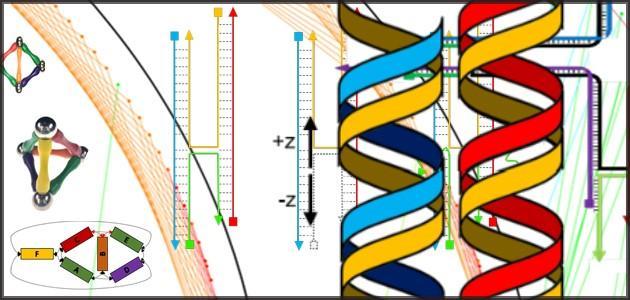
DNA折纸依赖于DNA分子互补碱基对彼此结合的能力。在DNA的四个碱基中-腺嘌呤(A),胞嘧啶(C),鸟嘌呤(G)和胸腺嘧啶(T)-A与T和G一起与C结合。这意味着As,Ts,Cs和Gs的特定序列将找到并绑定到其补语。
结合使DNA的短链可以充当“订书钉”,使长链的部分保持折叠状态或连接独立的链。典型的折纸设计可能需要250个订书钉。这样,DNA可以自组装成各种形状,形成一个纳米尺度的框架,各种纳米颗粒(许多在医学治疗,生物学研究和环境监测中有用的)可以附着在纳米框架上。
Majikes说,使用DNA折纸的挑战是双重的。首先,研究人员正在使用外语(碱基对A,G,T和C)制造3D结构。此外,他们正在使用这些碱基对的订书钉来扭曲和解旋熟悉的DNA分子双螺旋,从而使股弯曲成特定的形状。这可能很难设计和可视化。Majikes和Liddle敦促研究人员在开始制造之前,通过构建3D模型来增强设计直觉,例如用条形磁铁制成的雕塑。这些模型可以揭示折叠过程的哪些方面很关键,哪些方面不那么重要,然后应将其“展平”为2D,以与DNA折纸的计算机辅助设计工具兼容,该工具通常使用二维表示。
